
Tutorial
de RasMol sobre
Proteínas y DNA
a
a
Antes
de iniciar:
-
Se sugiere a los principiantes visitar primero el home page de
RasMol
www.umass.edu/microbio/rasmol.
Encontrarán sitios e información de gran interés
para los usuarios de RasMol,
acceso on-line a bancos de diferentes tipos de moléculas, animaciones
o scripts desarrollados por la comunidad de RasMol
y acceso gratuito al software de visualización molecular.
-
La versión original de este tutorial se encuentra en:
www.umass.edu/microbio/raswhat.htm
-
Aquí puede encontrar y bajar el archivo de coordenadas moleculares
de este tutorial : 1d66.pdb (Gal4: Factor
de Regulación Transcripcional - DNA).
Inicio :
-
En este tutorial se trabaja con aplicaciones de RasMol
empleando tanto el Menú de Herramientas de la Ventana de Gráficos
Principal, como también, usando la Línea de Comandos o Ventana
Auxiliar.
En el primer caso el comando estará precedido de la letra
M.
Los comandos se indican separados por (;) En la Línea de Comandos
deben escribirse manteniendo la sintaxis indicada, en líneas separadas
para cada comando seguidas por enter.
-
Los comentarios y explicaciones para cada grupo de comandos se indican
en letra cursiva.
-
Ejecute RasMol,
en el Menú File, dé la opción
Open seleccione el archivo 1d66.pdb
-
Capítulo
1
Preguntas
& Respuestas sobre 1d66.pdb
¿Cuántas cadenas
tiene 1d66.pdb?
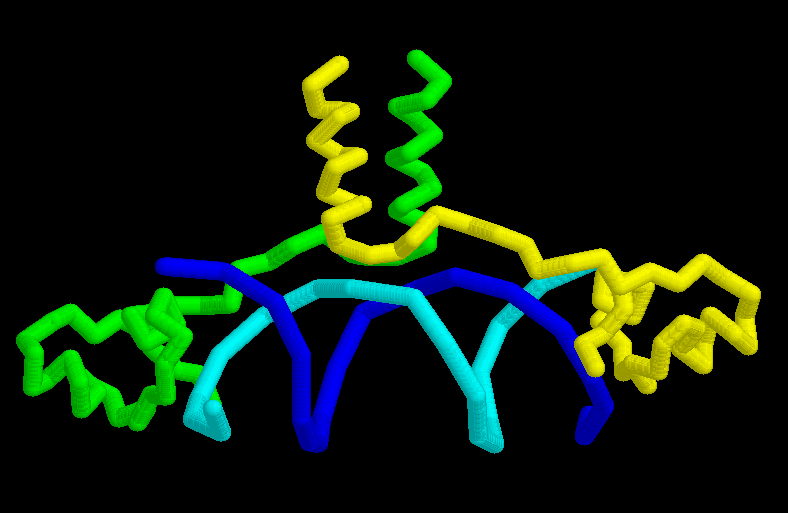 |
reset; rotate z 90; zoom 150; rotate y 40
Menú Display - Backbone
En el Menú Display puede cambiar la representación
de la molécula. En la opción "Backbone" se representa la
molécula como una línea trazada entre los átomos que
forman el enlace peptídico para las proteínas o como una
línea de unión entre los grupos de azúcar fosfato
para los ácidos nucléicos.
M Colours - Chain
Ahora cada cadena aparece en un color diferente. Al dar click sobre
cada Cadena en la Ventana de la Línea de Comandos aparece el código
ID del átomo correspondiente con su ubicación dentro de cada
cadena del archivo PDB.
|
¿Existe algo en el archivo PDB diferente
a Proteína y DNA?
-
select hetero; M Display
- Spacefill
-
espacio
|
-
Con la opción "Select Hetero", se visualizan los átomos
de oxígeno asociados al cristal de la molécula.
-
espacio
|
|
-
M Colours - CPK
-
espacio
|
|
-
En el Menú Colours es posible modificar el color de la representación
de la molécula. El esquema de Colores Cpk asigna un color a cada
elemento químico. Encontrará una descripción detallada
de los colores en el Manual de RasMol:
-
espacio
|
-
Sección Colores y Esquemas de Color.
-
espaci
|
-
restrict not water
-
espacio
|
-
Este comando oculta las moléculas de agua. Al dar click sobre
los átomos hetero se obtiene su identificación en la ventana
de la Línea de Comandos. En los archivos PDB puede encontrarse algunas
ambigüedades en la designación de los átomos, así
CD puede hacer referencia a un Carbono Delta o a un átomo de Cadmio.
-
espacio
|
-
¿Dónde se encuentran los aminoácidos
hidrofóbicos?
-
select hydrophobic; color magenta; wireframe 0.4
-
espacio
|
Observe la amfipaticidad de las a-
hélices. El diámetro de las representaciones moleculares
de RasMol puede modificarse con un valor numérico luego del comando,
en este caso "wireframe 0.4", que indica un diámetro en los enlaces
de 0.4 angstróms.
espacio
|
-
select not water; M Display - Spacefill;
M
Options M- Slab mode
-
espacio
|
-
Con la opción "Slab" se realiza un corte en el eje z sobre
la molécula de manera que sólo se observan las regiones ubicabas
por detrás del plano de corte. Esta representación permite
visualizar la disposición de los residuos al interior de la molécula.
Al mover con el mouse la molécula es posible cambiar la porción
de la molécula por detrás del plano de corte y observar la
ubicación de los aminoácidos hidrofóbicos.
|
¿Qué residuos están próximos
a los átomos de Cadmio ?
-
M Options - Slab mode
Desactive el modo slab
M Edit - Select All
-
M Display - Backbone; M
Colours
- Chain
select cd; M Display - Spacefill; M
Colours - CPK
select within(2.6, cd)
Este comando selecciona todos los átomos ubicados 2.6 Angstróms
alrededor de los iones de Cd+2
M Display - Spacefill; M
Colours - CPK
Al dar click sobre estos átomos se conoce su identidad
|
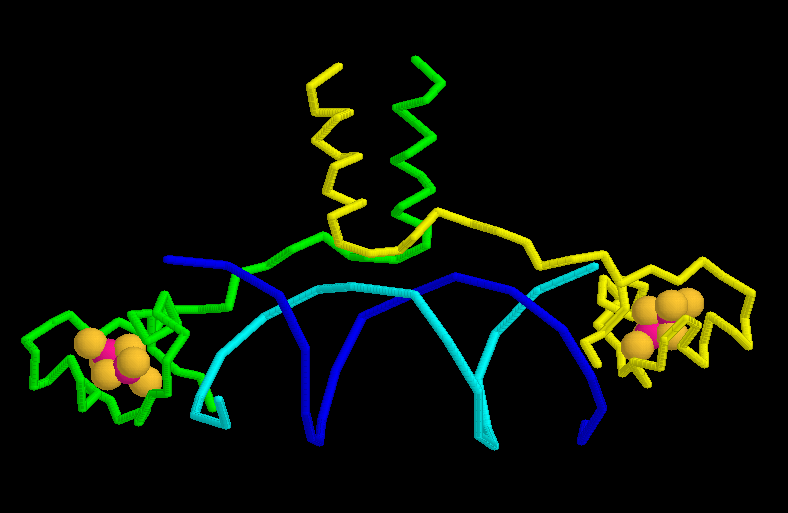 |
¿Cómo guardar esta representación
?
save script imagen1.spt;
M File - Close
|
Para volver a la imagen guardada :espacio
|
script imagen1.sptespacio
|
¿Cómo encontrar los segmentos
en a-hélice y en
hoja plegada b?
M Edit - Select all; M
Display - Backbone; M Colours - Structure
-
El esquema de RasMol Color Structure, asigna color según la estructura
secundaría. Así, las alfa hélices aparecen magenta,
las hojas beta en amarillo, los segmentos turn en azul y el resto de la
proteína en blanco.
-
structure; M Colours - Structure.
select protein, M Display - Cartoons
Observe la aparición de los segmentos "Turns".
|
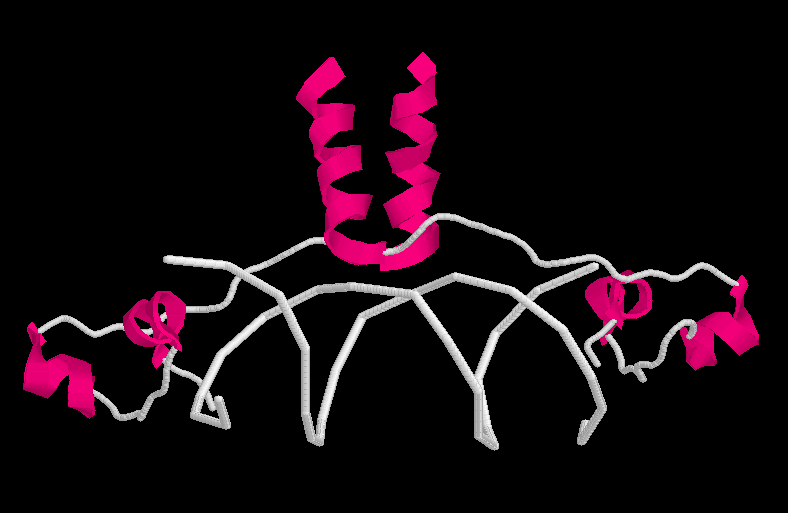 |
-
¿Cómo encontrar la distancia entre
dos átomos?
-
M Display - Spacefill; set picking distance
-
espacio
|
Ahora al dar click sobre dos átomos, en la ventana
de la Línea de Comandos aparece la distancia entre ellos en angstróms.
Para marcar la distancia en la ventana principal use el comando:
espacio
|
-
set picking monitor
-
espacio
|
-
Nuevamente click sobre dos átomos, esta aplicación puede
funcionar mejor con un fondo blanco de la pantalla. Observe entonces con:
-
espacio
|
-
background white
-
set picking ident
-
espacio
|
-
Esta opción habilita la propiedad de RasMol de identificación
de átomos al dar click sobre ellos. Con "Set picking" pueden medirse
ángulos y torsiones. Consulte las aplicaciones de este comando
en el Manual:
-
espacio
|
-
Sección Parámetros Internos
|
-
¿Cómo encontrar los puntos de interacción
entre la proteína y el DNA?
-
reset; M Display - Backbone;
color green; rotate z 91; translate y -17; zoom 200
select dna; color white; spacefill; center selected
select dna and backbone; color yellow
espacio
|
Aquí Ud., puede observar el DNA con el eje de azúcar
fosfato en amarillo y los pares de bases en blanco y puede observar el
esqueleto de la proteína como una delgada línea verde.
espacio
|
-
select within(3.1, dna) and not dna
-
espacio
|
Si Ud. omite la expresión "and not dna"
seleccionará también el DNA. Luego de este comando Ud. habrá
seleccionado sólo 35 átomos.espacio
|
-
dots
-
espacio
|
-
El comando dots, permite la representación de la superficie de
Van der. Waals de los átomos seleccionados.
|
-
Ahora oprima la fecha hacia arriba de su teclado, de forma que aparezcan
los comandos usados, hágalo hasta la línea del comando "within"
y al final agregue "and not water" al dar enter 19 átomos
deben ser seleccionados.
-
espacio
-
spacefill 1.2
-
color blue
-
Ahora los átomos que unen la proteína se visualizan como
pequeñas esferas sólidas con una superficie dots.Mientras
que los átomos de oxígeno de las moléculas de agua
se visualizan como esferas rojas.espacio
select within(3.1, protein) and dna; color cpk
|
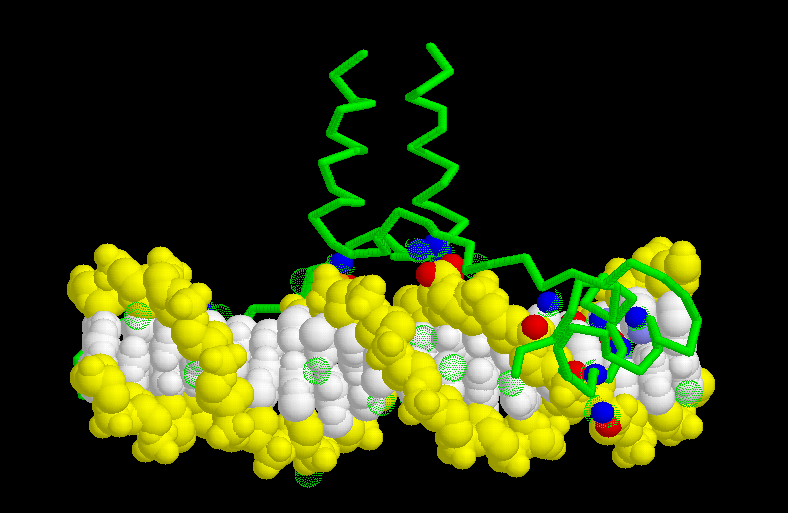 |
-
¿Cómo visualizar el interior de la
molécula?
Precaución: no mueva la molécula durante este
numeral.espacio
|
-
reset; M Edit - Select All;
M Display - Spacefill; M Colour - Chain.
rotate x 83; zoom 200
M Options - Hetero Atomsespacio
|
Desactive la opción heteroátomosespacio
|
select dna; color cpk;
M Options - Slab Mode
espacio
|
Active el modo Slab. La mitad de la molécula ha sido
cortada en el plano z, ahora sólo es posible visualizar lo que se
encuentra por detrás del plano de corte
espacio
|
-
set slabmode section
-
espacio
|
-
Ahora sólo se muestra la porción cortada de la molécula,
entre los planos del corte, todo lo que se encuentra por detrás
o por delante del plano de corte es ocultado.
-
espacio
|
-
slab 76
-
espacio
|
-
Ud. puede ver un par de bases GC, haga cortes en el plano para localizar
los tres puentes de hidrógeno, entre este par de bases.
-
espacio
|
-
slab 68
-
espacio
|
-
Qué es esto? Utilice el mouse para mover el plano de corte del
slab (oprima Ctrl, y luego click hacia arriba y hacia abajo). Puede encontrar
algún par de bases que no corresponda a las leyes de apareamiento
de Watson & Crick?. La respuesta al final de este tutorial.
|
Controlando
la representación molecular de RasMol
-
¿Cómo rotar la molécula alrededor
del DNA?
-
reset; restrict dna; rotate z 90; zoom 200
-
espacio
|
-
Trate de rotar la molécula alrededor de la doble hélice
del DNA (utilice el mouse). Observe como el DNA sube y baja según
la molécula rota alrededor de su centro de gravedad, incluyendo
a la proteína.
-
espacio
|
-
center selectedespacio
|
-
Ahora rote nuevamente la molécula y observe la diferencia en
el movimiento de rotación.
-
espacio
|
-
¿Cómo obtener diferentes representaciones
del mismo átomo?
-
restrict :d; M Colours - CPK
-
espacio
|
La expresión ":d" es un indicador de cadena, así,
el comando "restrict :d" hace que RasMol muestre solamente los átomos
ubicados sobre la cadena D del archivo PDB. Encontrará mayor
información sobre las expresiones de selección o restricción
en el Manual de RasMol :espacio
Sección Expresiones Atómicas.
espacio
|
-
M Display - Backbone, M
Display - Ball & Stick
-
espacio
|
-
Observe que cuando se emplea el Menú de Herramientas para cambiar
la representación de la molécula cada modelo inactiva el
anterior, a diferencia de cuando se asigna la representación por
comandos, en este caso cada nueva representación se agrega a la
ya establecida, de forma que es posible combinar modelos sobre una misma
región seleccionada de la molécula.
-
espacio
|
-
backbone 1.0
-
espacio
|
La representación en "Sticks" es la misma representación
en "wireframe" sólo que con un diámetro mayor de los enlaces.
La representación en "Balls" es una representación en "spacefill"
a la que se asignan el mismo radio para todos los átomos. Observe
ahora con:
|
-
spacefill off; wireframe 0.5; wireframe 0.1; spacefill 0.3; backbone
0.1; zoom 500
|
-
¿Cómo marcar los átomos?
-
set picking label
-
espacio
|
-
Haga click sobre algunos átomos.
-
espacio
|
-
label off; set picking ident
-
espacio
|
-
Para marcar un átomo, este debe seleccionarse primero, entonces
haga click sobre el átomo que desee marcar y observe cuál
es su número ID, el número de la átomo en la molécula,
por ejemplo:
-
espacio
-
CA 1197
Group Arg 60 Chain A
-
espacio
-
Significa que el átomo corresponde al Carbono Alfa - Número
1197, que pertenece al residuo de Arginina 60 de la Cadena A . Entonces
para seleccionarlo
-
espacio
|
-
select atomno=1197; label "Este es mi atomo"
-
|
-
Es posible cambiar el tamaño de la fuente en un intervalo de
1-32 (pixeles) y el color del texto. Utilice para ello:
-
espacio
|
-
set fontsize 20
-
color labels white;
-
label off
|
Capítulo
2
Explorando
la Molécula de su interés.
Antes
de iniciar:
-
Utilice un editor de texto normal como Word o el Bloc de Notas para
abrir el archivo PDB. este archivo contiene información sobre las
características estructurales de la molécula. Si desea mayor
información consulte : Propiedades
de los archivo PDB
-
Ejecute RasMol, en el Menú File,
dé la opción Open seleccione el archivo PDB.
¿Cuántas cadenas posee la molécula?
-
M Display - Backbone;
M
Colour - Chain
-
espacio
|
-
En cualquier momento usted puede restringir la visualización
a una o varias cadenas del archivo PDB. Para identificar las cadenas debe
hacer click sobre los átomos y obtener su identificación
ID. Por ejemplo para ocultar todas las cadenas excepto la B y D, use el
comando
-
espacio
|
-
restrict :b or :d .
-
espacio
|
-
Para restablecer la visualización de todas las cadenas.
-
espacio
|
M Edit,
Select allespacio
|
Si prefiere trabajar sólo con una parte del archivo
PDB puede ser útil hacer una copia del archivo PDB sólo con
los segmentos de su interés. Para hacerlo debe seleccionar los átomos,
cadenas, residuos o ligandos en RasMol con el comando "select" y luego
guardar el nuevo pdb con el comando:
espacio
|
Save nuevo.pdb
espacio
|
Abra entonces el nuevo PDB en el menú File - Open,.
tenga en cuenta que en RasMol sólo puede cargar una molécula
a la vez, por ello debe cerrar el PDB inicial.
|
¿Hay algún Ligando en la molécula?
-
select hetero; M Display - Spacefill; M
Colour - CPK
-
espacio
|
-
Haga click sobre las moléculas hetero para obtener el código
de residuo ID de tres letras. En algunos archivos PDB puede encontrarse
información sobre los ligandos presentes, utilice un editor de texto
normal como Word o el Bloc de Notas para abrir el archivo.
-
espacio
-
En algunas ocasiones la visualización del archivo puede ser obstruida
por los átomos de oxígeno de las moléculas de agua
asociadas al cristal de la proteína (Recuerde que los hidrógenos
no son resueltos por Difracción de Rayos X). La mayoría de
estas moléculas de agua se difunden aleatoriamente en el cristal
haciendo que la representación de la molécula sea confusa.
Por ello es conveniente restringir la visualización a los átomos
que hacen parte de la proteína, usando el comando:
-
espacio
|
restrict not water .
|
-
¿Cuál es la Estructura Secundaria?
-
M Display - Cartoon; M
Colour - Structure
-
espacio
|
-
El esquema de RasMol Color Structure, asigna color según la estructura
secundaría. Así, las alfa hélices aparecen magenta,
las hojas beta en amarillo, los segmentos turn en azul y el resto de la
proteína en blanco.
espacio
Algunos archivos PDB tienen registros para la estructura secundaría
de la proteína denominados HELIX y SHEET, si esto ocurre RasMol
obedece estos segmentos, pero si el archivo PDB no específica la
estructura secundaría, el comando "structure" lo obliga a determinarla
mediante la utilización de algoritmos apropiados.
|
¿Dónde se encuentran los extremos
N y C-Terminal?
-
M Colour - Group.
-
espacio
|
-
La representación en "Backbone" es la más apropiada para
este numeral. Con el esquema de Colores Group
-
cada cadena es coloreada desde el extremo azul, cambiando en el orden
de los colores del arco iris, al verde, amarillo y naranja hasta rojo en
su otro extremo. Si la molécula se observa en azul use la opción:
-
espacio
|
-
M Options - Hetero atoms
-
espacio
|
-
Desactive la visualización de los heteroátomos, luego
nuevamente
-
espacio
|
-
M Colour - Group.
-
espacio
|
Aquí una forma mnemotécnica para recordar
el significado de la escala de colores en el esquema Colour Group
espacio
-
Blue = cold = old (N terminal de la proteína, extremo 5' del
ácido nucléico)
-
Red = hot = new (C terminal de la proteína, extremo
5' del ácido nucléico)
-
El extremo Amino Terminal tiene el color CPK azul del nitrógeno
y el extremo Carbóxilo Terminal tiene el color CPK rojo del oxígeno.
|
-
¿Dónde están las cadenas laterales
de los residuos hidrofóbicos?
-
M Edit - Select All; M Display - Spacefill
-
select protein; color [180,180,180]
-
select protein and backbone; color [100,0,100]
-
select protein and not (backbone or hydrophobic); color magenta
-
espacio
|
El comando "color" puede utilizarse especificando el color
deseado con el nombre en inglés o con el código RGB, que
consiste en una combinación de valores numéricos, en escala
del 0 al 255, de los colores, rojo, verde y azul. De esta forma pueden
combinarse los valores para obtener una gama de 256 colores.
Para completar su visualización , puede usarespacio
|
-
select not protein; color greenblue
-
espacio
-
|
-
A los átomos que conforman el "Backbone" o el eje de la proteína
usualmente se les asigna un color magenta oscuro indicando que son débilmente
hidrofóbicos. Los grupos R de los aminoácidos hidrofóbicos
son grises para indicar su alto contenido de carbono. Los grupos R de los
residuos cargados y/o polares se muestran en magenta brillante indicando
su naturaleza hidrofílica. El magenta es usado para representar
un mezcla de partes iguales de rojo y azul (según la carga, rojo
para O=positivo y azul=N negativo).
-
espacio
-
Los largos segmentos de cadenas laterales hidrofóbicas en la
superficie de una proteína, indican que estas regiones pueden hacer
contacto con moléculas diferentes al agua, como por ejemplo en la
interacción de subunidades de una proteína multimérica
o proteínas que están unidas o rodeadas por lípidos.
|
¿Dónde están los Puentes
Disulfuro?
-
M Display - Wireframe; ssbonds 0.8
-
espacio
|
-
Los puentes disulfuro se visualizan ahora como cilindros con un radio
de 0.8 Angstróms. El color de la representación puede cambiarse
con los comandos:
-
espacio
|
-
color ssbonds yellow.
-
espacio
|
-
La primera vez que se usa el comando se reporta el número de
puentes disulfuro de la molécula: si no se observa ninguno posiblemente
se debe a que en la región seleccionada no se encuentra ninguno
de los residuos de Cistina. La solución es entonces :
-
espacio
|
-
M Edit - Select All .
-
M Display - Backbone; M Colour - Chain
-
espacio
|
-
Ahora sólo se observan los carbonos alfa en los residuos de Cisteínas
que forman puentes disulfuro. Los puentes de disulfuro, por defecto se
trazan entre los átomos de azufre, y estos no se observan con la
representación en Backbone, para evitar que los puentes se observen
flotando entre las cadenas de proteína y observarlos desde el eje
de la molécula:
-
espacio
|
-
set ssbonds backbone.
|
¿Dónde están los Puentes
de Hidrógeno?
-
M Edit - Select All; M
Display - Backbone; M Colour - Structure
-
restrict helix; backbone 0; hbonds 0.5; color hbonds white
-
espacio
|
-
RasMol mostrará solo los puentes de hidrógeno entre los
átomos del enlace peptídico, omitiendo los que se forman
entre las cadenas laterales, los ligandos , los sitios de unión,
etc. al igual que los puentes disulfuro, los de hidrógeno se representan
flotando entre los ejes "backbone" de la proteína, pero pueden trazarse
desde los carbonos alfa de cada residuo con el comando
-
espacio
|
-
set ssbonds backbone
-
ssbonds off
-
espacio
|
-
Ahora repita la secuencia anterior de comandos pero reemplazando la
restricción de las hélices por la de las hojas beta, use
por ejemplo
-
espacioespacio
|
-
restrict sheet como también
-
restrict not (helix or sheet).
-
espacio
|
-
¿Dónde están los Puentes Intercatenarios?
Los puentes entre Ligando-Proteína?
-
Para encontrar los puentes de hidrógeno entre motivos estructurales,
debe usarse el comando "within" como se hizo en el ejemplo del archivo
1d66.pdb. Un puente de hidrógeno tiene una longitud de 3.0
Angstróms entre los átomos donor y aceptor por ejemplo N
y O, tomando en cuenta 1.0 angstróm del enlace covalente del hidrógeno
y 2.0 angstrom del puente de hidrógeno. Entonces una distancia de
3.0 ó 3.2 angstróms es apropiada para el comando "within".
Los puentes hidrófóbicos (carbono) tienden a ser más
largos, hasta de 4.0 Angstróms.
|
El apareamiento incorrecto del numeral 10, slab 53 corresponde la
posición C28. No existe razón para creer que la posición
de este residuo se deba a una interacción inusual con los residuos
cercanos, ni a que este resíduo no obedezca las leyes de apareamiento
postuladas por Watson & Crick.
La única explicación es que no hay que creer todo en
un archivo PDB, sólo porque a un átomo el archivo asigne
una posición precisa dentro de la molécula, no significa
que esta posición sea correcta.
 RasMol
y Chime
RasMol
y Chime




